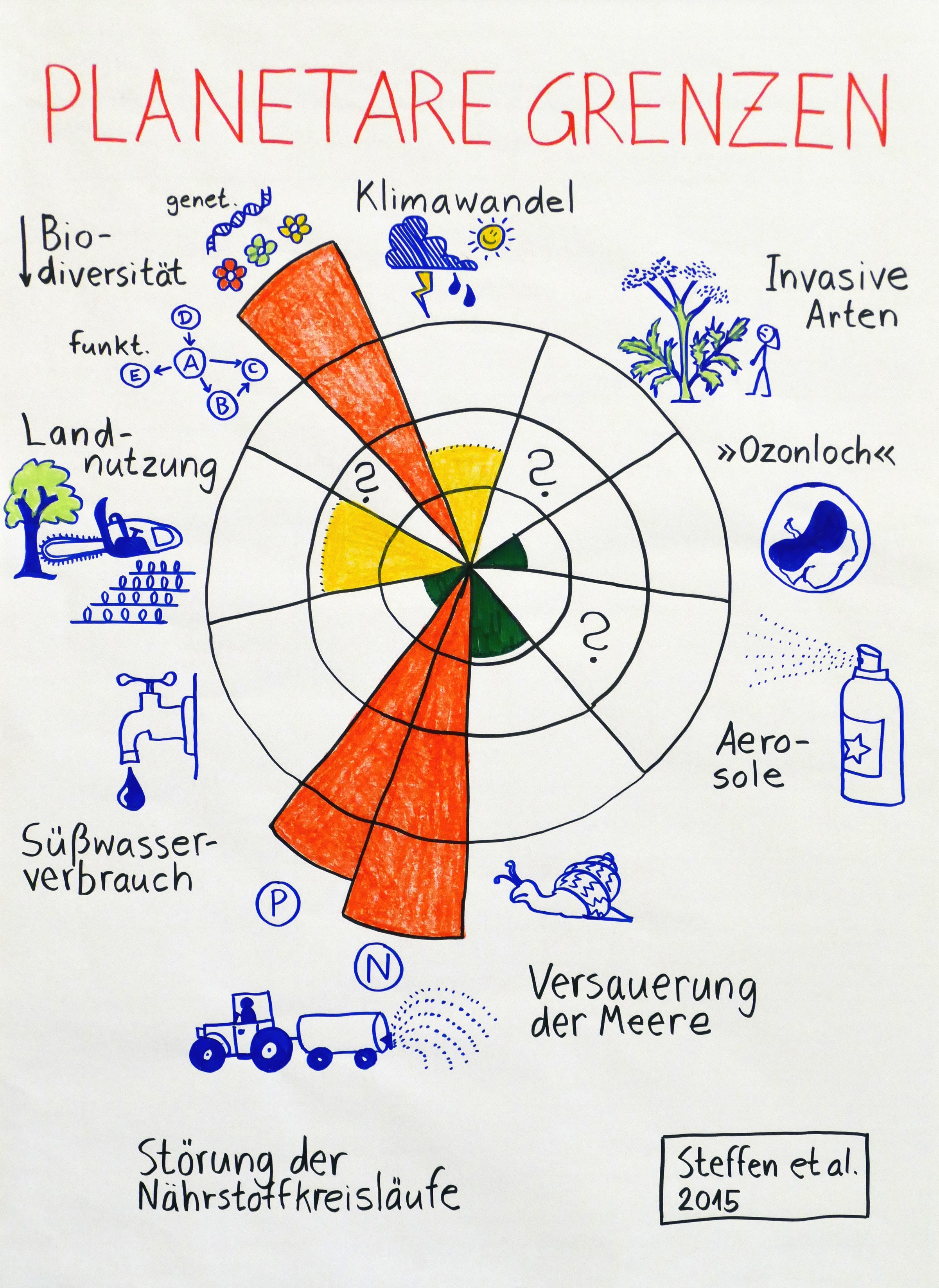
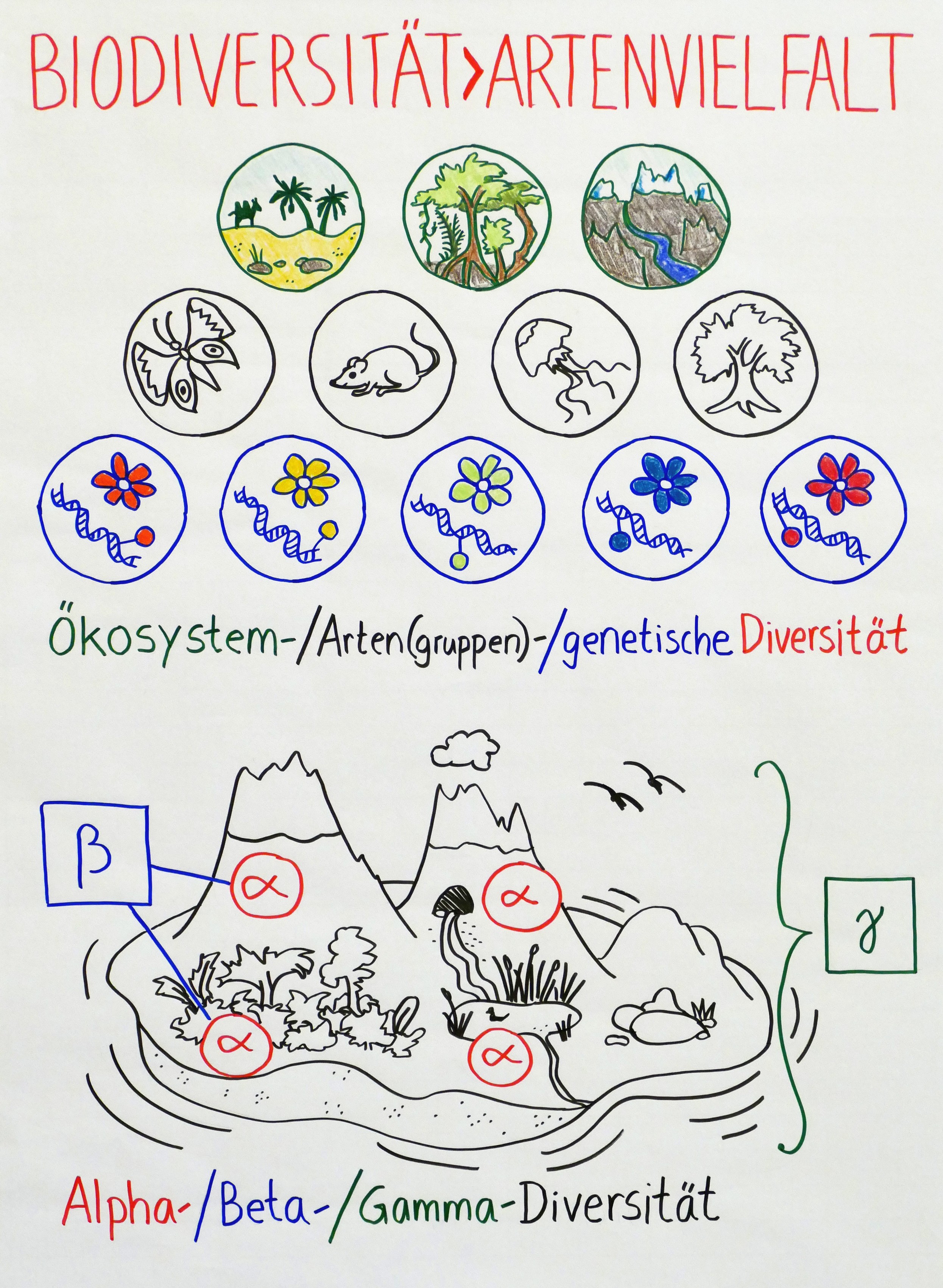
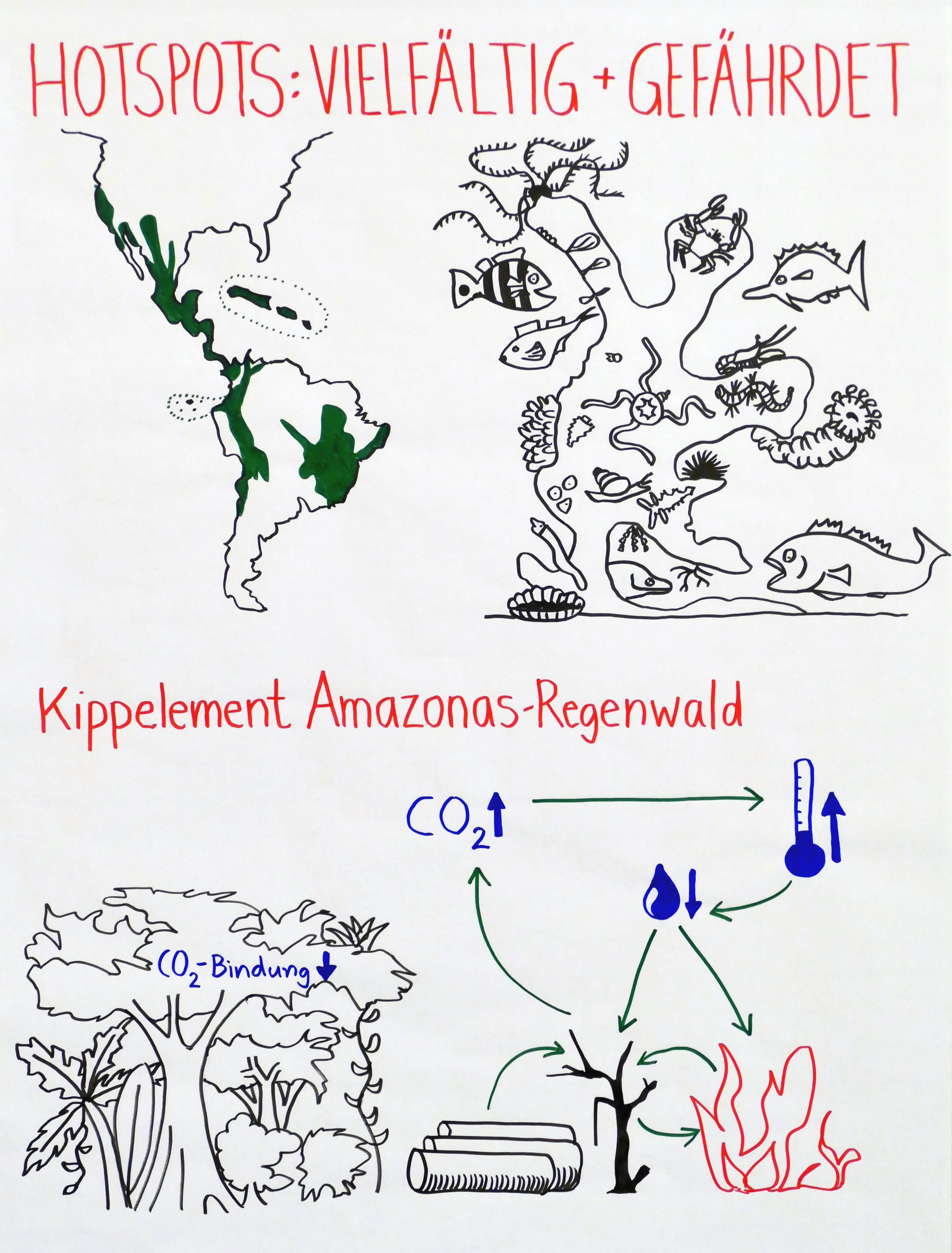
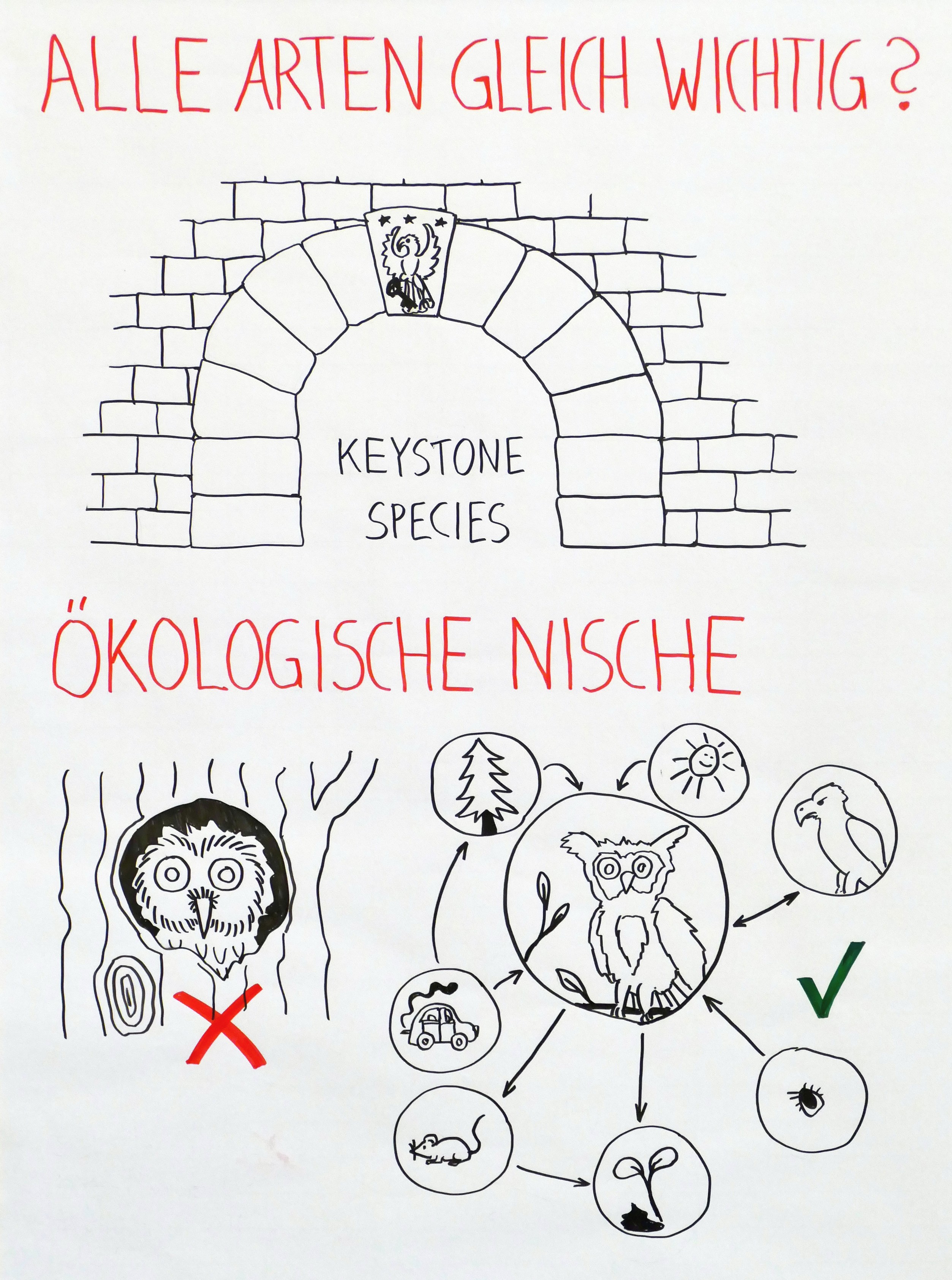
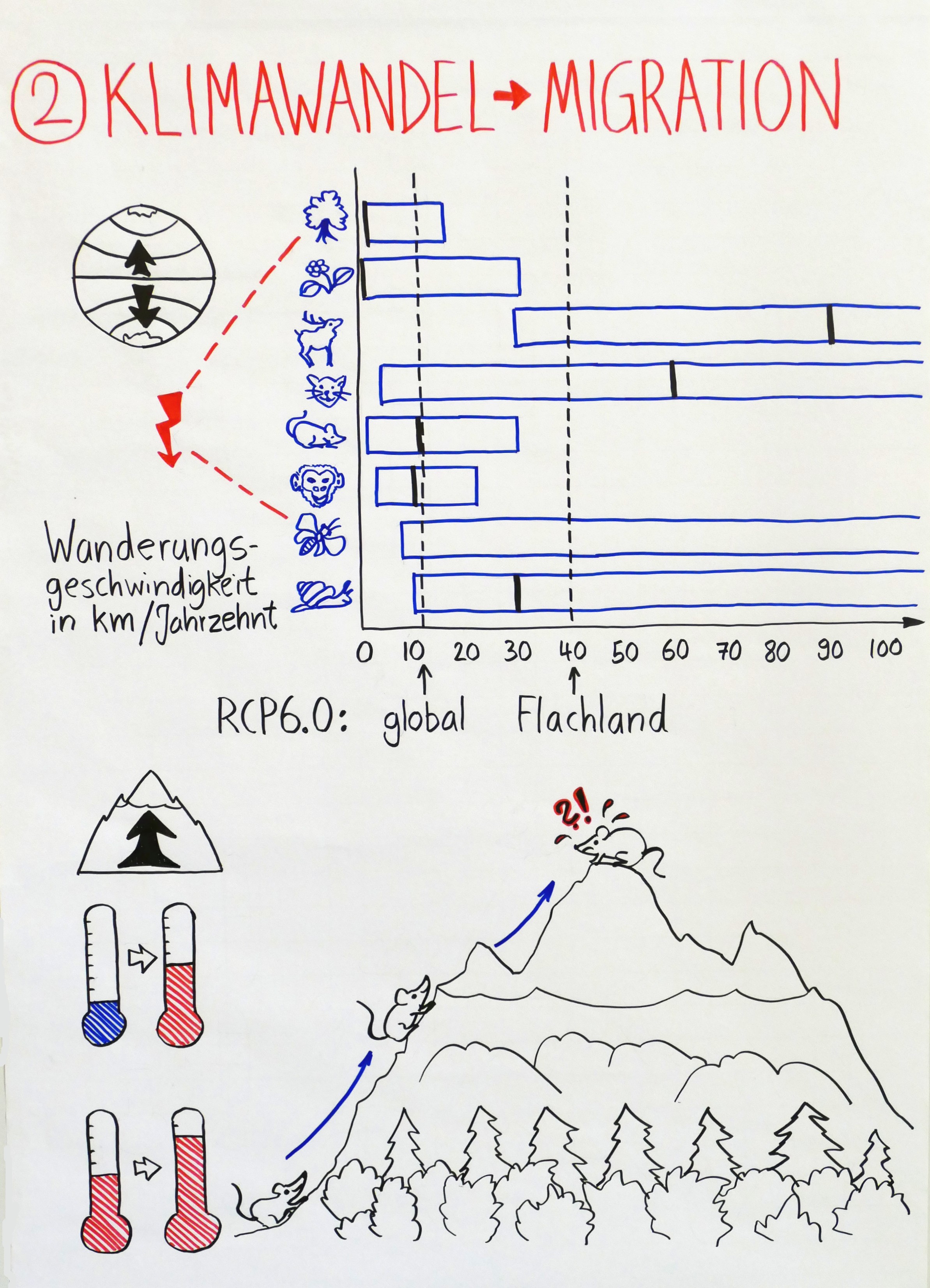
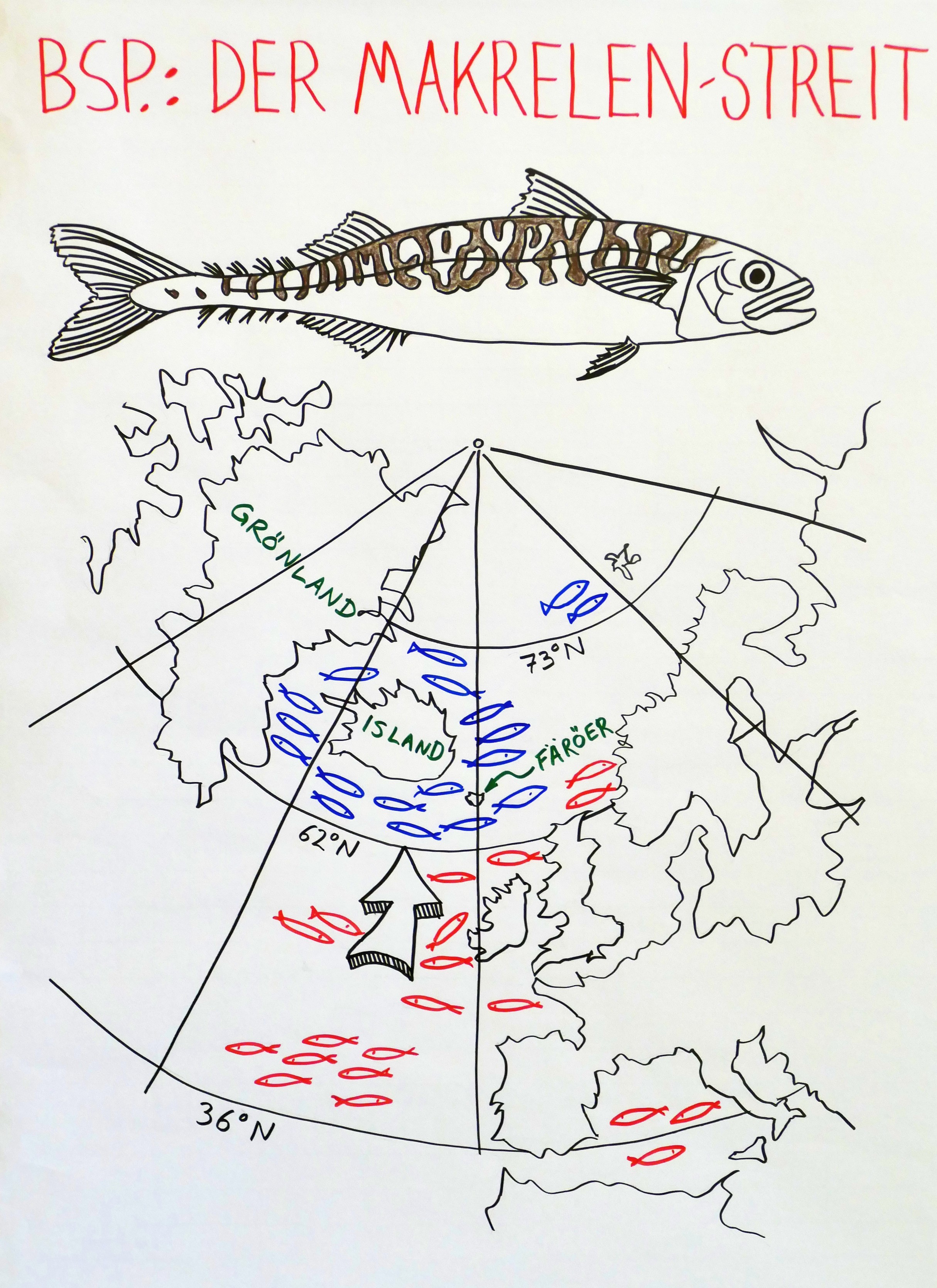
Zwischen meiner Rückkehr aus Dortmund, wo ich heute beim Sommerkongress von „Fridays for Future“ einen Workshop zu Biodiversität und Klimawandel gegeben habe, und meinem Aufbruch in den Urlaub liegen nur wenige Stunden. Daher veröffentliche ich hier zunächst Fotos meiner 14 Flipchart-Blätter und der 20 Definitionskarten, vor allem als Gedächtnisstütze für Teilnehmerinnen und Teilnehmer.
Ohne Erläuterungen sind die Blätter schwer verständlich: Ich bin erklärte Gegnerin von Präsentationen, bei denen die Referentin oder der Referent mehr oder weniger vorliest, was auf den Powerpoint-Folien oder auf dem Flipchart-Block steht. Erst die Kombination aus gesprochenem Wort und den Bildern (Infografiken, Cartoons, Diagrammen, Allegorien …) ergibt eine sinnvolle Einheit.
Nach dem Urlaub werde ich hier wenigstens Stichworte nachtragen, damit etwas klarer wird, worüber ich gesprochen und mit der Gruppe diskutiert habe.
Meine wichtigste Quelle war dieses Fachbuch: Thomas E. Lovejoy und Lee Hannah (Hg.): Biodiversity and Climate Change – Transforming the Biosphere. Yale University Press, 2019